Étiquette : GenBank
-
Bioconvert - simplifier les conversions de formats
Bioconvert Qui n'a jamais eu à convertir un fichier de données biologiques dans un autre format ? Il y a bien sur le classique fastq vers fasta, pour lequel nombre d'entre nous ont codé un convertisseur "maison", pas forcément optimal. D'autres formats sont parfois plus problématiques, par exemple la conversion vers et depuis GFF2/GFF3. De ces différents…
-
Automatiser la récupération de données biologiques
Qui dit bioinformatique, dit récupération et manipulation des données. Ces données peuvent être générées à partir d'algorithmes ou bien récupérées depuis des bases de données biologiques. Aujourd'hui, le nombre de ces bases de données est en constante augmentation. Chaque mécanisme biologique, famille moléculaire ou organisme est associé à un ou plusieurs de ces dépôts de données. Si un…
-
Soirée BED & FASTA !

Après la petite histoire de l’analyse des séquences d’ADN, voici un tutoriel pour apprendre quelques trucs et astuces dans ce domaine. Biologiste en mal de connaissances de programmation ou pro de R, vous trouverez ici de quoi vous amuser avec un fichier Fasta ou un Bed. Nous allons voir comment faire un alignement multiple de…
-
Astuce programmation BioPython : Parser les multi-genbank et les multi-FASTA produits par Batch Entrez
Prérequis : Savoir 'un peu' se servir d'un shell et avoir installé Python et son module Bio. But : Redécouper des multi-genbank ou des multi-FASTA en un fichier par entrée. Difficulté : 2/5 (Facile) Principe : Le NCBI propose un outil très pratique pour récupérer facilement des jeux de données diversifiés : BatchEntrez, vous trouverez plus d'information ici. On télécharge ainsi un…
-
Récupérez facilement des données hébergées par le NCBI : BatchEntrez
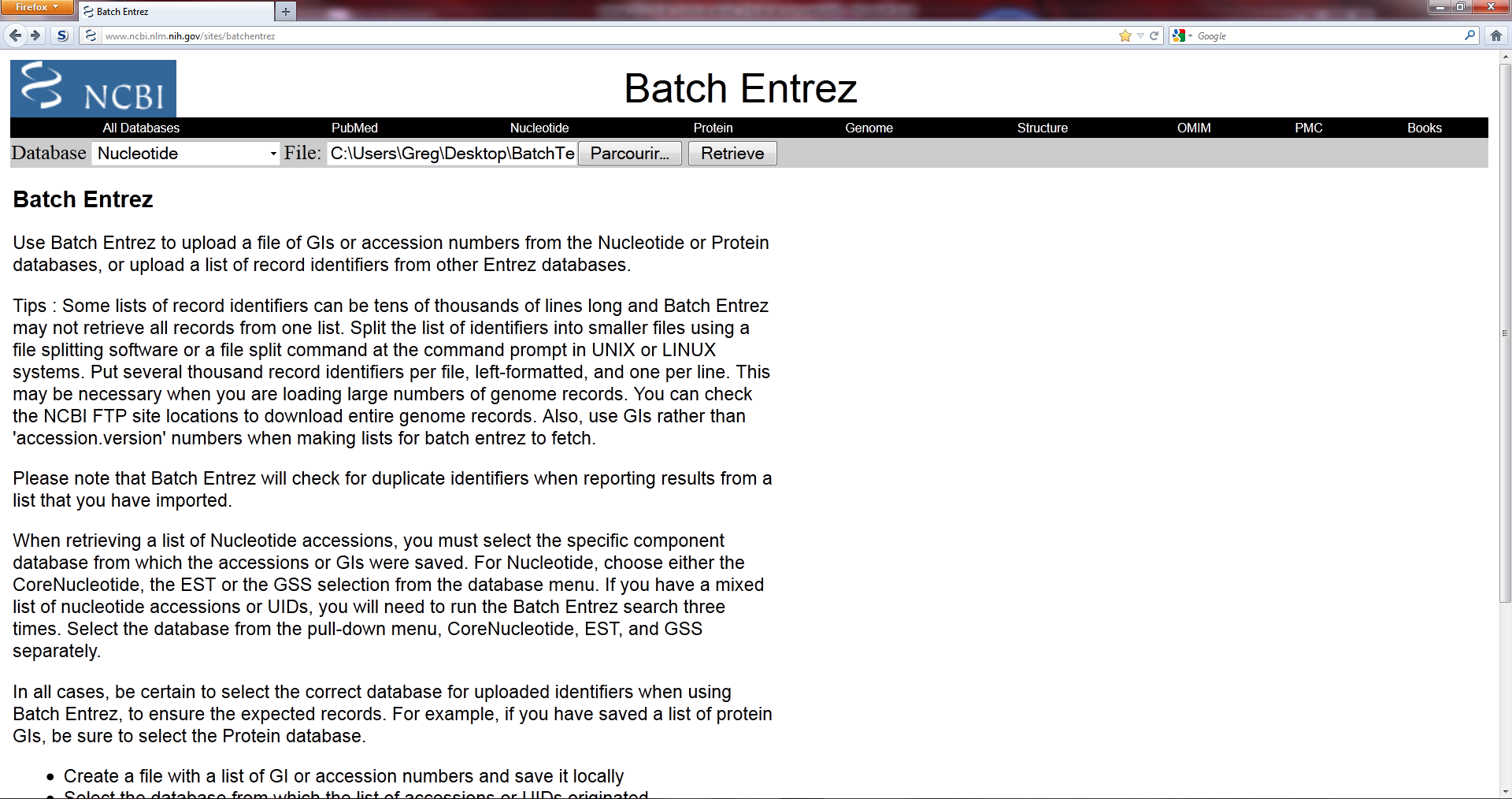
But : Les bases de données du NCBI abritent de très nombreuses informations : génomes, protéines, références bibliographiques, etc. Si vous souhaitez récupérer l'une d'entre-elles, une recherche sur le site est la solution la plus simple, mais si vous avez besoin de récupérer de nombreuses données dans un des formats proposés, alors le NCBI a mis l'outil…
-
Transformer une sortie de Blast xml en format GenBank
Bonjour, et bienvenu dans mon premier article concernant mon script Perl Blast2Gb.pl. Ce dernier illustre parfaitement ce qu'on peut faire facilement et rapidement avec un script Perl : du traitement de texte. Cet outil permet de faciliter la vie et de transformer une tâche laborieuse en un traitement rapide et efficace. En effet, qui ne s'est…

