Catégorie : Découverte
-
La fin du génome linéaire : Bienvenue dans l'ère (complexe) du Pangénome
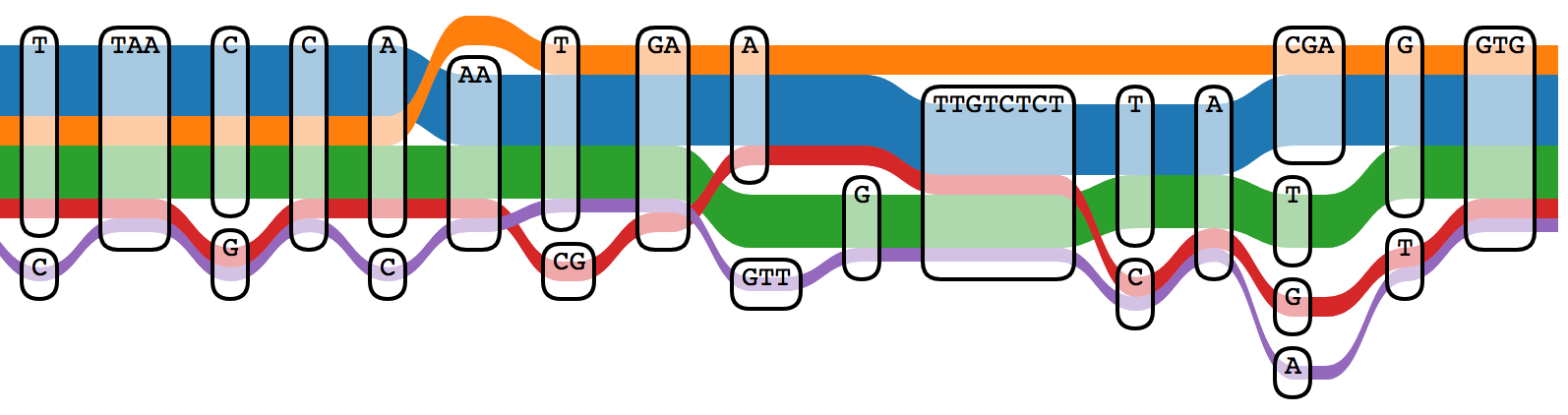
Que vous soyez bio-informaticien aguerri, étudiant en master ou simplement curieux ayant déjà manipulé un fichier FASTA un jour dans votre vie, ce billet de blog est pour vous. Nous allons explorer pourquoi et comment nos repères actuels en génomique sont en train de changer de forme. Le génome de référence classique Prenons l'exemple du…
-
La complexité inattendue des systèmes de coordonnées en bioinformatique
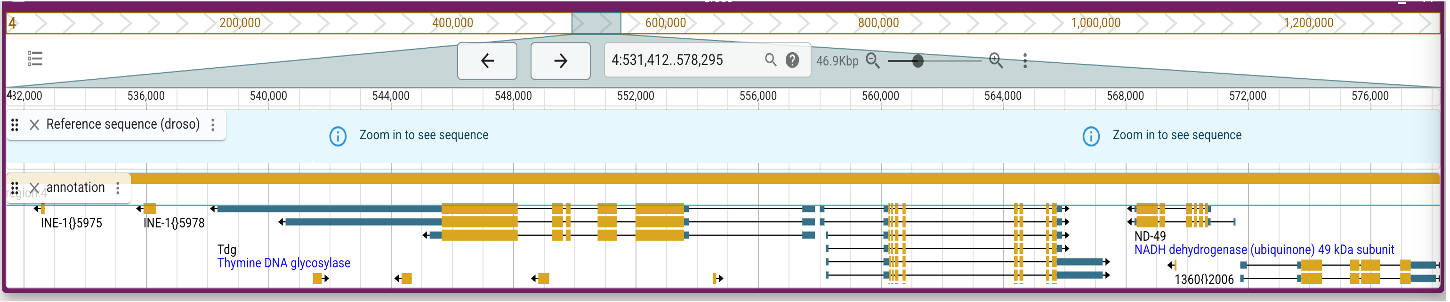
En bioinformatique, quand on manipule des génomes, des annotations, des fichiers d’alignement, des variants ou des intervalles (exons, régions régulatrices, etc.), on est rapidement confronté à deux notions fondamentales qui conditionnent la manière dont les positions sont décrites et interprétées : Ces deux dimensions définissent ensemble le système de coordonnées utilisé. Les maîtriser permet d’interpréter correctement…
-
Trois exemples concrets qui m'ont fait m'intéresser à la reproductibilité entre langages
Mes très chers confrères adorés, Comme vous le savez si vous lisez mes excellents articles d'opinion, tous géniaux (hum !), cela fait quelques années maintenant que je travaille pour des toxicologues. Alors, c'est bien, j'ai appris plein de choses, au point de me définir aujourd'hui comme « computational toxicologist ». Mais j'ai surtout mis mon nez dans…
-
L'alignement multiple en étoile ⭐
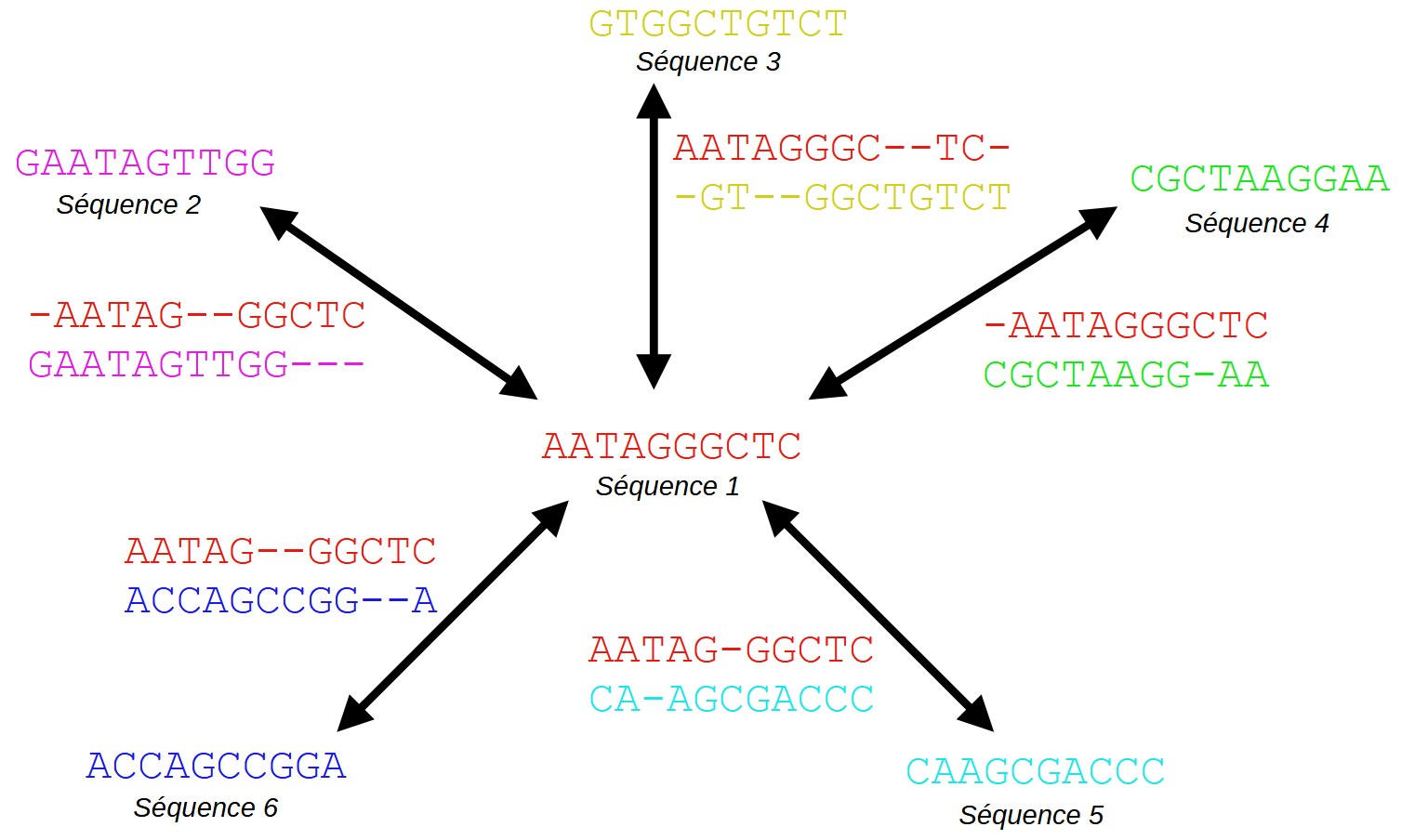
Introduction Dans le domaine de la bioinformatique l'alignement de séquences est une opération courante pour comparer des séquences biologiques (ADN, ARN, protéines). Nous avons vu dans un précédent article le principe de l'algorithme de Needleman-Wunsch qui produit un alignement global optimal de deux séquences. Au-delà de l'alignement par paire, l'alignement multiple de séquences (Multiple Sequence…
-
Alignement de séquences : bien comprendre l'incontournable algorithme de Needleman-Wunsch
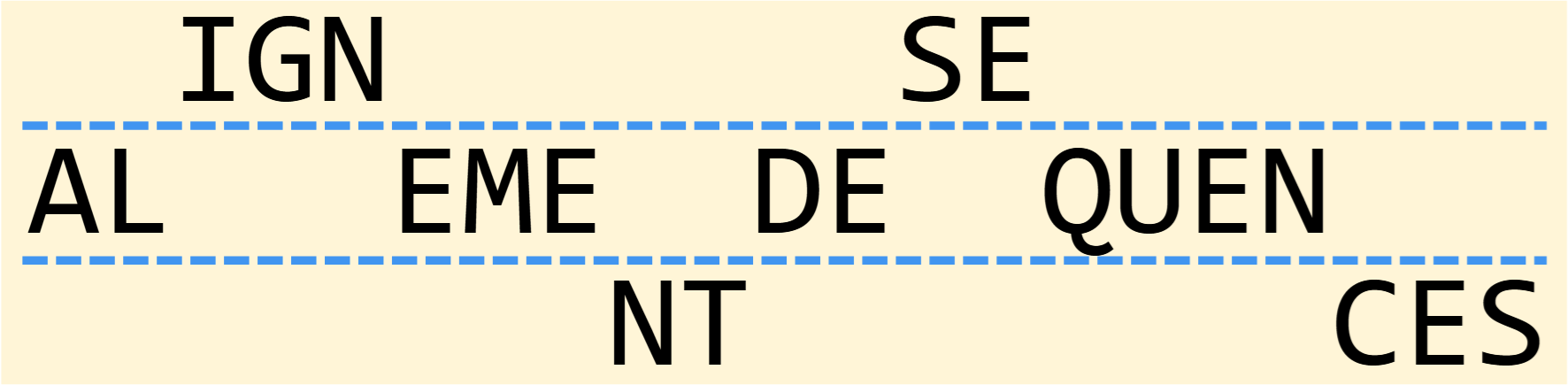
Introduction L'analyse des séquences biologiques (ADN, ARN ou protéines) est un sujet central de la biologie moléculaire et de la bioinformatique. Dans ce cadre, chercher à savoir à quel point deux séquences sont similaires ou dissimilaires est une des questions qu'on se pose le plus souvent (par exemple dans le but d'analyser des relations phylogénétiques).…
-
Des molécules et des données !
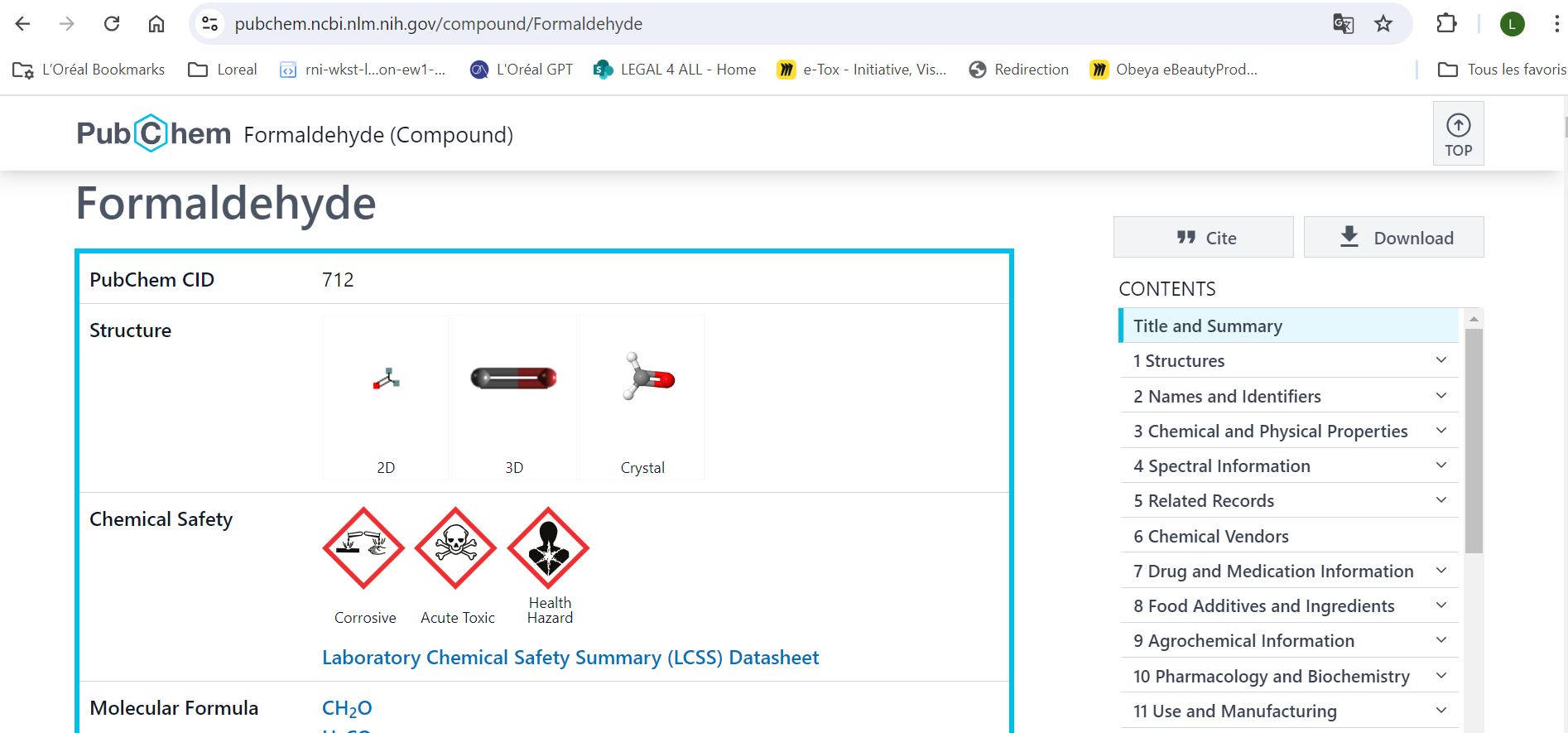
Vu que nous sommes sur un blog de bio-informatique, je vous propose aujourd'hui de parler chimie ! Enfin plutôt, chémoinformatique* et quelques notions de la façon dont une molécule est stockée en ligne en fonction des réglementations chimiques et cosmétiques. Je ne suis pas un expert de ce domaine, mais alors vraiment pas du tout. Par…
-
Software Heritage : l'archive universelle des codes sources logiciels
Dans cet article, je vous propose de découvrir Software Heritage, l’archive universelle dédiée à la collecte, la préservation et le partage des codes sources logiciels. En 2021, je suis devenu ambassadeur pour Software Heritage, c’est-à-dire représentant de la communauté bioinformatique, dans l’infrastructure Software Heritage. Pourquoi archiver son code source ? Aujourd’hui, les scientifiques utilisent très souvent des…
-
ABSD : base de données d'anticorps non redondants et standardisés

Les anticorps (immunoglobulines) jouent un rôle crucial dans la réponse immunitaire contre les menaces extérieures, telles les infections virales. Une immunoglobuline est composée de deux molécules en interaction appelées chaîne légère et chaîne lourde : la combinaison d’une chaîne légère et d’une chaîne lourde donne une immunoglobuline (voir Figure 1). Bien que le nombre théorique d'immunoglobulines…

